基于R的linkET包qcorrplot可视化Mantel test相关性网络热图分析correlation heatmap
写在前面
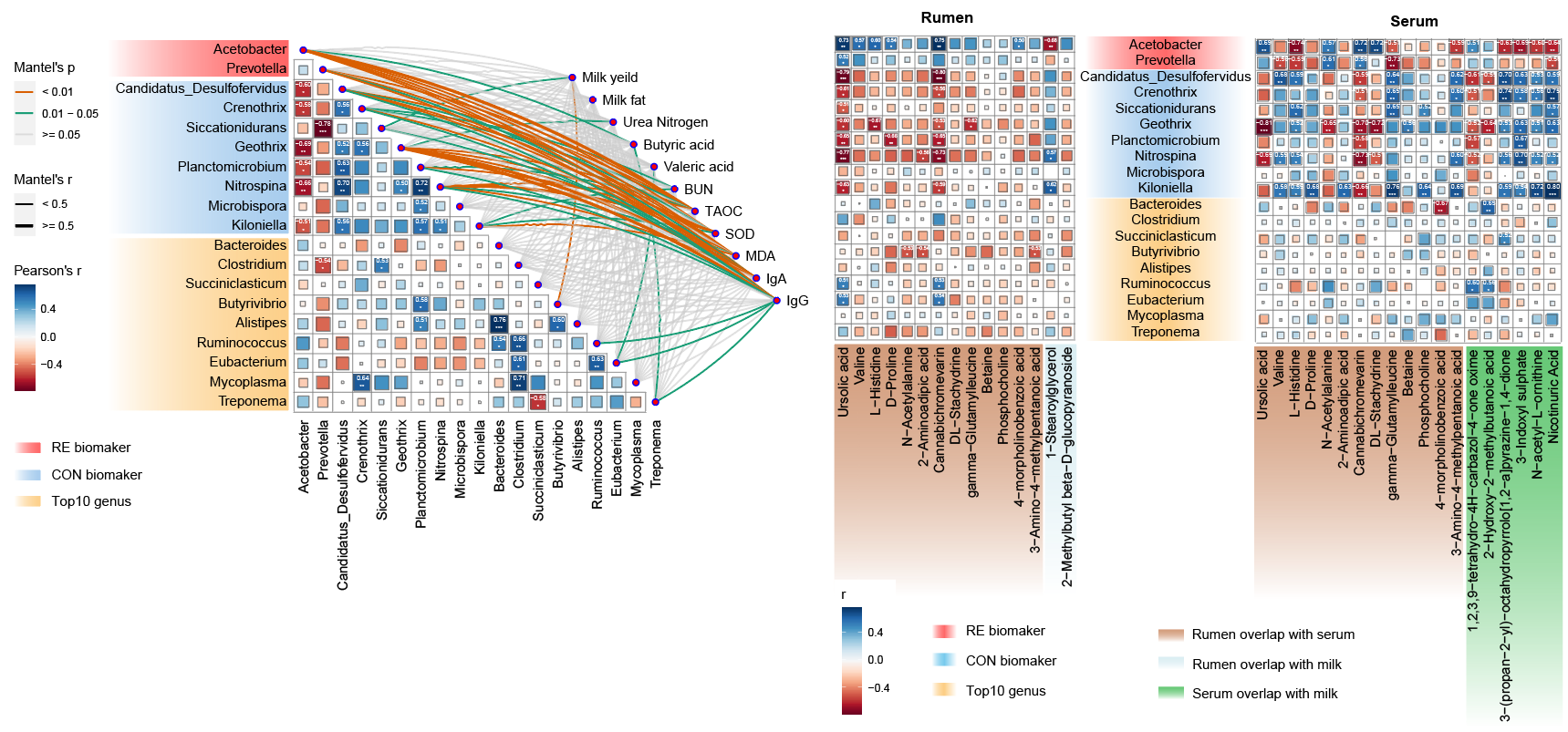
需求是对瘤胃宏基因组结果鉴定到的差异菌株与表观指标、瘤胃代谢组、血清代谢组、牛奶代谢组中有差异的部分进行关联分析,效果图如下:
数据准备
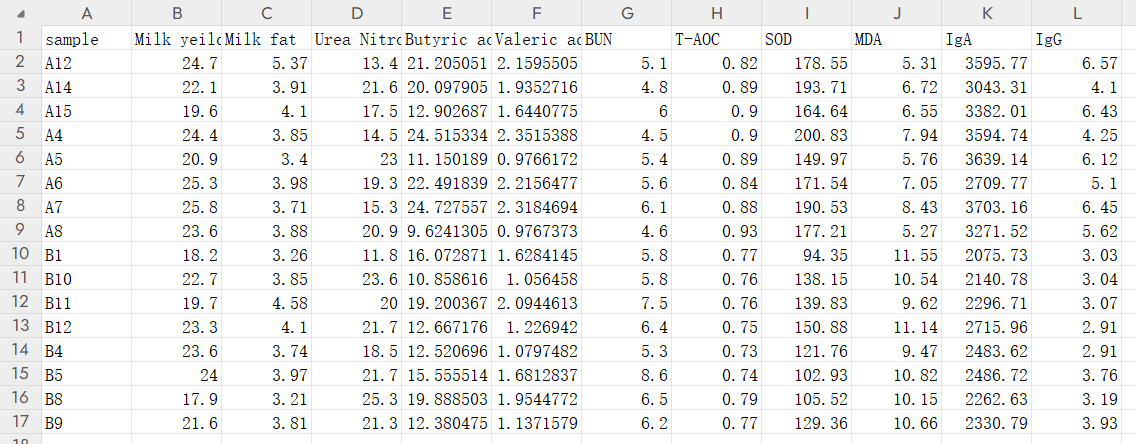
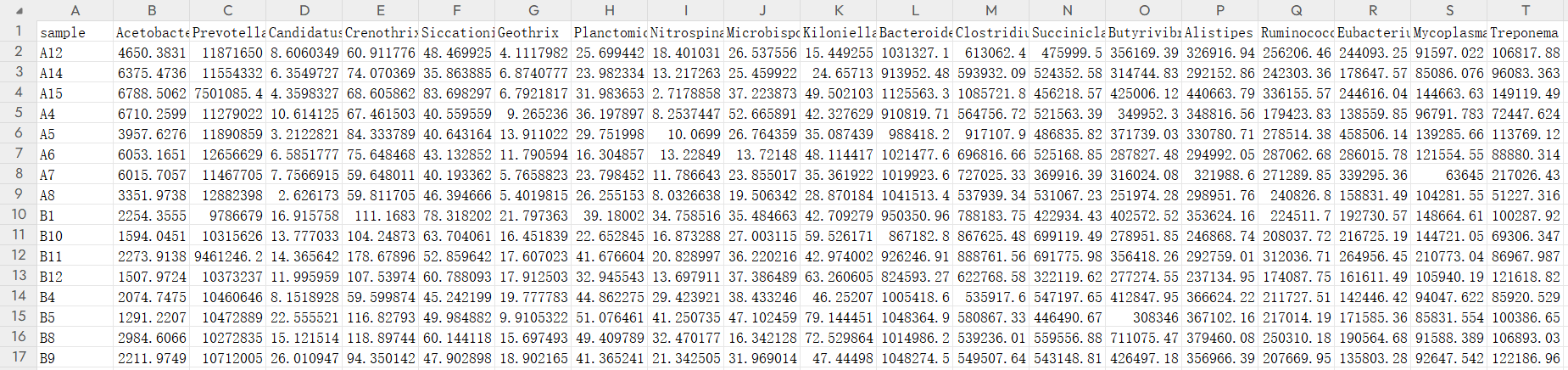
逗号分隔的csv格式文件,两个表格,一个是每个样本对应的表观指标数据,另一个是每个样本对应的菌群丰度,我这里用的是genus水平
- 需要关联的表观数据
rumen.csv
- 不同样本的菌群丰度
genus.csv
R包linkET可视化
- 装包
install.pakages("linkET")
library(linkET)
如果报错R版本有问题装不上(我的4.3.1版本R出现了这个报错)请尝试:
install.packages("devtools")
devtools::install_github("Hy4m/linkET", force = TRUE)
packageVersion("linkET")
- 读取数据
library(ggplot2)
rumen <- read.csv("rumen.csv",sep=",",row.name=1,stringsAsFactors = FALSE,check.names = FALSE)
genus <- read.csv("genus.csv",sep=",",row.name=1,stringsAsFactors = FALSE,check.names = FALSE)
#如果报错row.names重复错误请检查数据格式是否为csv
rumen.csv组内相关系数
matrix_data(list(rumen = rumen)) %>% as_md_tbl()
correlate(rumen) %>% as_matrix_data()
correlate(rumen) %>% as_md_tbl()correlate(rumen) %>% as_md_tbl() %>% qcorrplot() +geom_square()#如果对“%>%”功能报错,装具有此功能的包即可,比如dplyrlibrary(vegan)
correlate(rumen, genus, method = "spearman") %>% qcorrplot() +geom_square() +geom_mark(sep = '\n',size = 3, sig_level = c(0.05, 0.01, 0.001),sig_thres = 0.05, color = 'white') + #添加显著性和相关性值scale_fill_gradientn(colours = RColorBrewer::brewer.pal(11, "RdBu"))
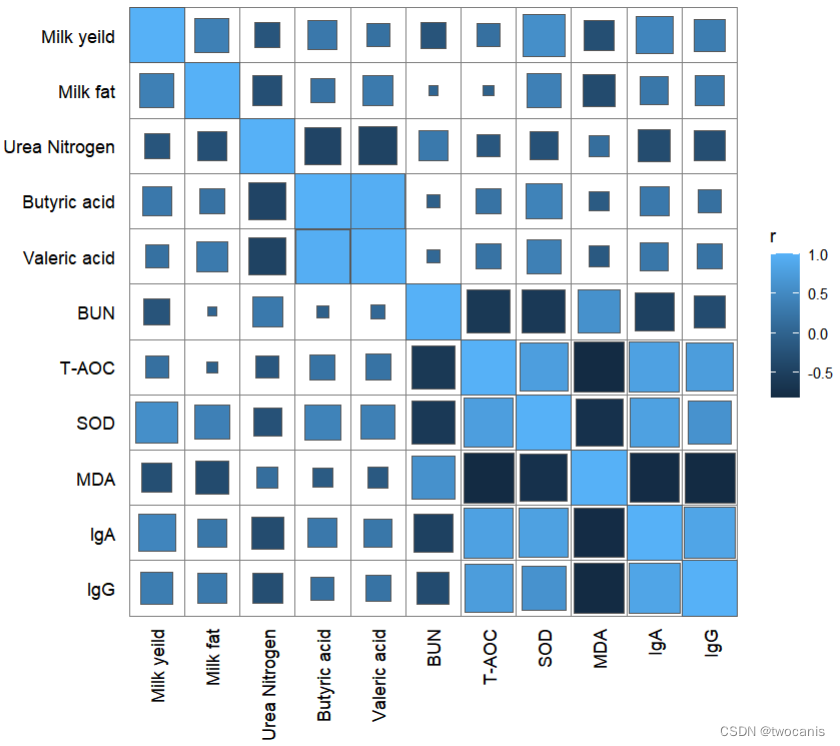
- 两个表格进行关联生成相关性矩阵图,带显著性标记
library(vegan)
correlate(rumen, genus, method = "spearman") %>% qcorrplot() +geom_square() +geom_mark(sep = '\n',size = 3, sig_level = c(0.05, 0.01, 0.001),sig_thres = 0.05, color = 'white') + #添加显著性和相关性值scale_fill_gradientn(colours = RColorBrewer::brewer.pal(11, "RdBu"))
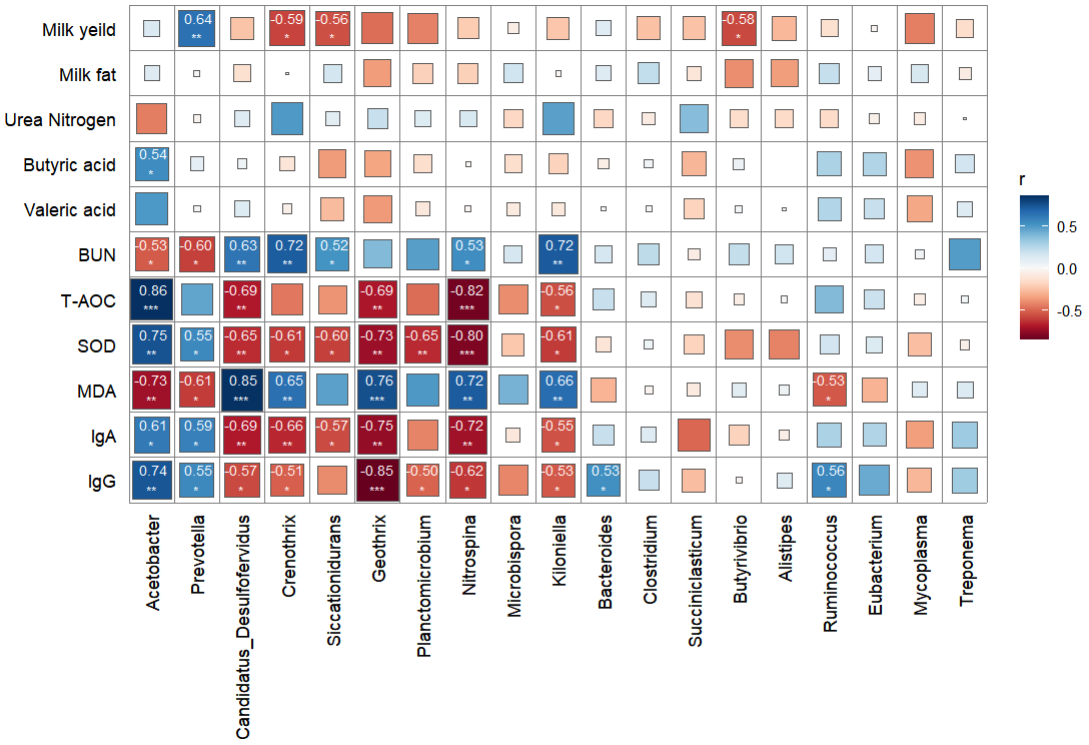
- 加工可视化
library(dplyr)
mantel <- mantel_test(rumen, genus,spec_select = list(Milk_yeild=1,Milk_fat=2,Urea_Nitrogen=3,Butyric_acid=4,Valeric_acid=5,BUN=6,T_AOC=7,SOD=8,MDA=9,IgA=10,IgG=11))%>% mutate(rd = cut(r, breaks = c(-Inf, 0.5, Inf),labels = c("< 0.5", ">= 0.5")),pd = cut(p, breaks = c(-Inf, 0.01, 0.05, Inf),labels = c("< 0.01", "0.01 - 0.05", ">= 0.05")))qcorrplot(correlate(genus), type = "lower", diag = FALSE) +geom_square() +geom_mark(sep = '\n',size = 1.8, sig_level = c(0.05, 0.01, 0.001),sig_thres = 0.05,color="white") +geom_couple(aes(colour = pd, size = rd), data = mantel, curvature = nice_curvature()) +scale_fill_gradientn(colours = RColorBrewer::brewer.pal(11, "RdBu")) +scale_size_manual(values = c(0.5, 1, 2)) +scale_colour_manual(values = color_pal(3)) +guides(size = guide_legend(title = "Mantel's r",override.aes = list(color = "black"), order = 2),colour = guide_legend(title = "Mantel's p", override.aes = list(size = 3), order = 1),fill = guide_colorbar(title = "Pearson's r", order = 3))
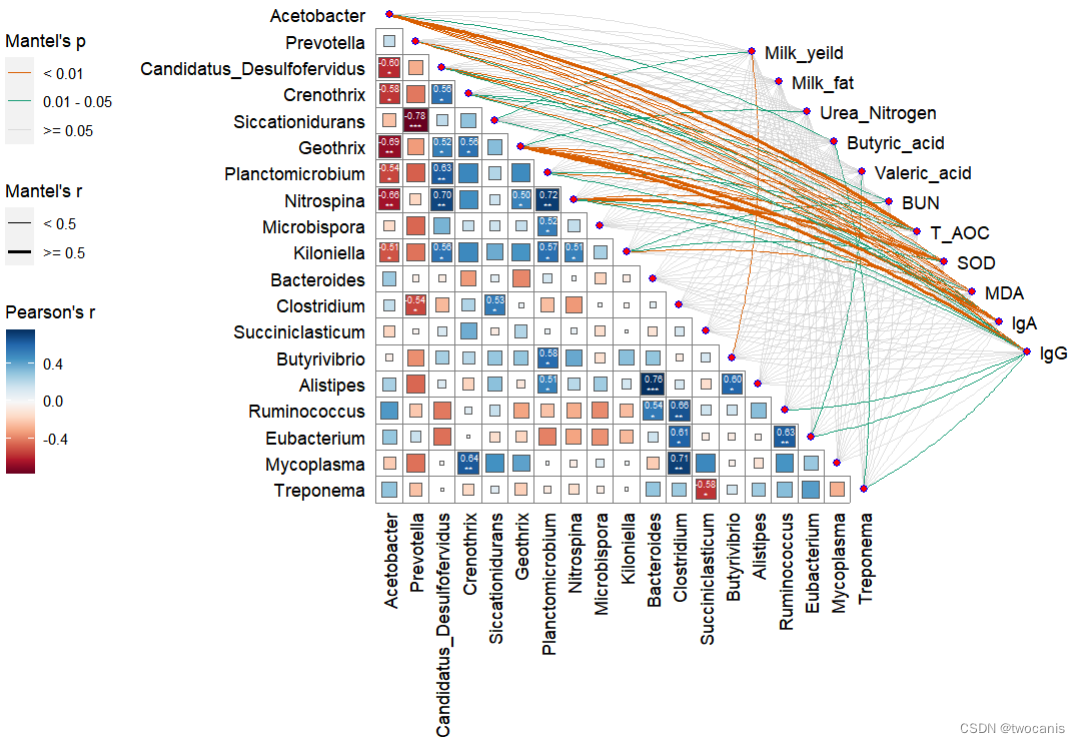
- 不显著的灰色连接线部分也可以去掉让画面更干净。其余细节去AI加工即可。
